La información del ADN
Compresión, longitud y la historia de una foto robada
La vida sucumbe irremisiblemente al deterioro al que toda estructura está condenada en el universo. La entropía acaba ganándole siempre la batalla, porque el estado desordenado e indiferente es el más probable de los estados. Por más longevos que sean los ejemplares de ciertas medusas, álamos o tiburones1, la segunda ley de la termodinámica es implacable y finalmente siempre acaba devorándolos entre sus fauces, aunque durante milenios logren sobrevivir en los medios más hostiles, incluso regenerándose cuanto pueden hasta finalmente desaparecer.
Sin embargo, como en un gesto insumiso que se rebela contra esa entropía, la vida propaga su complejidad desafiante transmitiendo como herencia la información misma que la estructura y se halla codificada en su ADN. Aunque la interpretación informativa de esta macromolécula es controvertida y responde en buena medida al momento tecnológico del último siglo en que vivimos, comprender el ADN como una estructura de información codificada para tejer un nuevo ser vivo, su complexión, su crecimiento y hasta su comportamiento es una idea potente y fecunda. Una idea que nos sobrevive después de muertos.
El disco duro que llevamos a cuestas
El ADN contiene una cantidad extraordinaria de información genética que actúa como un cierto manual de instrucciones útil para construir y mantener a un ser vivo. Desde mediados del siglo XX, cuando la biología molecular comenzó a describir la vida en términos de códigos, secuencias y transmisión de información, el genoma se ha interpretado cada vez más como un sistema de almacenamiento comparable — aunque infinitamente más compacto — a los dispositivos digitales creados por los humanos.
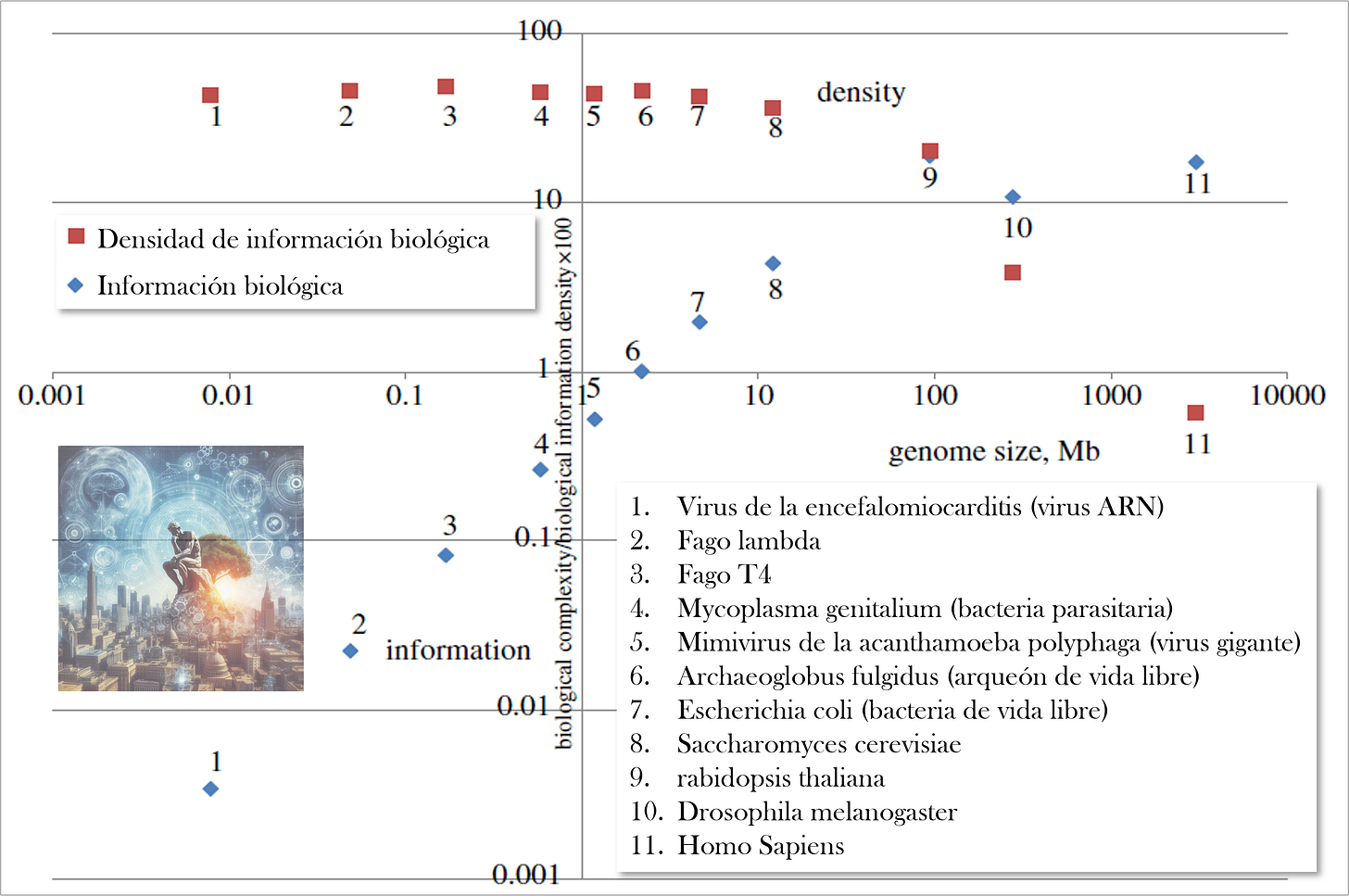
Estimar cuánta información contiene exactamente depende de cómo se mida. La unidad básica del ADN es el par de bases formado por cuatro nucleótidos posibles (A, T, C y G). Bajo esta métrica, el genoma humano posee aproximadamente 3.200 millones de pares de bases, según los resultados consolidados del Proyecto Genoma Humano y revisiones posteriores. Aunque la densidad informativa que atesoran es increíblemente mayor. Basta entender que el 99% de nuestro genoma coincide con el de los chimpancés, y hasta un 50% es idéntico al de los plátanos. Nos jugamos mucho en muy poco.
Si cada par de bases se representara digitalmente utilizando dos bits de información (la cantidad mínima necesaria para codificar cuatro estados posibles), el genoma humano haploide contendría alrededor de 6.400 millones de bits, es decir, unos 800 megabytes de información, aproximadamente equivalentes a los que ocupa uno de los ya casi obsoletos CD-ROM. Sin embargo, las células humanas son diploides, lo que significa que poseen dos copias completas del genoma: una heredada de la madre y otra del padre. En términos informáticos, cada una de las minúsculas células de nuestro cuerpo alberga por tanto cerca de 1,6 gigabytes de información genética.
Este cálculo, sin embargo, es solo una aproximación posible porque, en realidad, la información biológica no se limita a la secuencia lineal de nucleótidos, ni los rasgos fenotípicos se corresponden uno a uno con los genes: en la información biológica también intervienen patrones epigenéticos, estructuras tridimensionales del ADN y redes de regulación génica que multiplican la complejidad informativa del sistema. Pero de una forma u otra puede decirse que el ADN es, en cierto sentido, el alfabeto de la vida, en un sentido mucho más profundo que el de un mero texto inerte: es un programa de software que se ejecuta en el contexto de la célula.
Para ello, la naturaleza ha hecho del ADN el sistema de almacenamiento conocido más eficiente. Comprime en una molécula de apenas dos nanómetros de ancho una cantidad de información que deja en evidencia a las tecnologías convencionales de almacenamiento digital. Aunque ya existen líneas de investigación en almacenamiento molecular sobre ADN sintético, impulsadas por grandes laboratorios, que han logrado codificar libros, imágenes, películas e incluso sistemas operativos completos en secuencias artificiales de nucleótidos. Estas codificaciones después pueden ser sintetizadas, conservadas durante largos periodos y posteriormente leídas mediante técnicas de secuenciación genética. Sin embargo, probablemente acabe siendo necesario que el almacenamiento digital abandone el espacio electrónico del silicio para adentrarse en el tamaño cuántico de la nanotecnología y así poder competir con la increíble capacidad del ADN para comprimir información.
De hecho, su capacidad de compresión es tal que se estima, por ejemplo, que un solo gramo de ADN puede almacenar hasta 215 petabytes (215 millones de GB) de datos. Si sumáramos la información de todas las células del cuerpo humano (unos 37 billones), aunque gran parte sería información repetida, el volumen total ascendería aproximadamente a los 150 zettabytes, el orden de magnitud de toda la información generada y almacenada por la humanidad en toda su historia.
A pesar de su estrechez nanométrica, de hecho, el hilo que formaría el ADN de una sola célula si lo desplegásemos mediría unos 2 metros, y si se encadenase al del resto de sus compañeras en nuestro cuerpo, podría viajar y regresar varias veces hasta la Luna. Sin embargo, solo un pequeño porcentaje, alrededor del 2%, de nuestro ADN contribuye con información significativa para la codificación de proteínas. El resto es lo que durante décadas se ha conocido como ADN basura. Aunque hoy sabemos que no lo es tanto.
La densidad informativa y la utilidad del ADN basura
El llamado ADN basura (o ADN no codificante) constituye la inmensa mayor parte de nuestro genoma y durante mucho tiempo se pensó que se trataba de un material inútil acumulado por la evolución. Sin embargo, hoy sabemos que funciona como un reservorio de variabilidad y un sistema de control crucial para la supervivencia en entornos cambiantes. Porque el ADN no codificante, en primer lugar, protege a los genes importantes. El ADN es dañado unas 10.000 veces al día por agentes químicos o por radiación, y muta espontáneamente de forma imprevisible. Pero al tratarse de “ruido” y no de información, es estadísticamente más probable que esa mutación dañina caiga en una zona no crítica y no en un gen esencial. Y es además especialmente robusto pues, de hecho, el ADN puede conservarse durante cientos de miles de años, llegando a alcanzar incluso los 400.000 años de antigüedad como se ha comprobado con algunas muestras.
Pero, además, el ADN no codificante actúa como un espacio donde la naturaleza puede experimentar sin riesgo y preparar un buen repositorio de soluciones no probadas que sacar de la chistera ante un evento que desafíe la capacidad de adaptación de la vida. Al no fabricar proteínas vitales, este ADN puede permitirse el lujo de acumular variabilidad en secuencias con una “libertad de experimentación” que le permite “guardar” cambios genéticos que no son a priori útiles en el presente, pero que podrían resultar valiosos si el entorno cambiase. De este modo, muchas de estas regiones podrían convertirse con el tiempo en exaptaciones, es decir, en estructuras o secuencias que originalmente no tenían una función adaptativa clara o la tenían para otro propósito obsoleto pero que la evolución reutiliza posteriormente para cumplir con nuevas funciones biológicas.
El crecimiento de la información en la historia evolutiva puede observarse en el aumento de la cantidad de ADN de las distintas especies surgidas en el árbol biológico. Aunque en ese mismo crecimiento se observe una disminución de la densidad informativa precisamente para dar cabida a las ventajas de este ADN no codificante:
Por otra parte, gran parte de este ADN actúa como el sistema operativo del genoma, regulando cuándo y cómo se activan los genes. Actúan, en cierto modo, como sensores del entorno, ayudando a las células a reaccionar ante estímulos externos2. Y esto ocurre especialmente cuando las condiciones se vuelven extremas y llegan a activar partes del ADN transferido que a priori no era codificante pero que pueden desencadenar una serie de herramientas genéticas adicionales, por ejemplo en plantas expuestas a un particular estrés ambiental3.
Esta relación entre el ADN y la resiliencia es central. De hecho, buena parte del ADN no codificante, aproximadamente la mitad, proviene de antiguos virus que se integraron en nuestro ADN hace millones de años. Aunque estos fragmentos no están en su inmensa mayoría activos, han moldeado nuestra evolución y nos suministran una biblioteca — como los datos de entrenamiento de un LLM — de estrategias heredadas tras los encuentros pasados con patógenos. O, como diría Nietzsche, lo que no nos mata, nos hace más fuertes. Y esa resiliencia fue también clave en el descubrimiento de su estructura, una de cuyas artífices fue injustamente ninguneada.
Una foto robada
Como es bien conocido, la estructura del ADN fue desentrañada en 1953 por James Watson y Francis Crick y acabó mereciendo el reconocimiento con el premio Nobel de Medicina en 1962. Pero nada de este triunfo habría sido posible sin que una mujer proporcionara, sin reconocimiento alguno durante muchos años, la evidencia que permitió alumbrar la estructura acertada.
En 1952, Rosalind Franklin era una experta en cristalografía de rayos X y, dentro de sus investigaciones, logró capturar la famosa “Fotografía 51”. Esta imagen permitía intuir con gran claridad que la estructura que el ADN debía formar era la de una doble hélice con las bases enfrentadas en su interior. Pero Franklin fue prudente y prefirió confirmar completamente sus cálculos y el análisis de difracción antes de publicar formalmente los resultados asociados a aquella fotografía.
Maurice Wilkins era compañero de Franklin en el King’s College. Un día, Watson y Crick fueron a visitarle, presentándole una estructura para el ADN con la que estaban especulando y que resultaba errónea, tal y como Wilkins les hizo ver. Para avalar su argumento, y sin una solución alternativa, Wilkins echó mano de la fotografía de Rosalind sin su conocimiento, y se la mostró a los futuros laureados. Al ver la imagen, Watson comprendió rápidamente la estructura. Poco después, en 1953, Watson y Crick publicaron su famoso artículo en la revista Nature, uno de los artículos más influyentes de la historia de la ciencia. Aunque mencionaron el trabajo de Franklin, e incluyeron su imagen, la referencia fue más que limitada. La forma helicoidal se convirtió en un icono.
En 1958, la entropía hizo de las suyas, y a Rosalind Franklin, que apenas tenía 37 años, la barrió de la faz de la Tierra a través de un cáncer de ovario. Lo desarrolló muy probablemente por su exposición continua a las radiaciones asociadas a sus investigaciones, siendo fiel al espíritu comprometido por la ciencia de la mismísima Marie Curie.
Cuatro años después, en 1962, Watson, Crick y Wilkins recibían el Premio Nobel de Medicina, y el reconocimiento le era por completo hurtado a Franklin, tanto porque no puede concederse de forma póstuma — como le ocurrió a Tversky — como porque no podía compartirse entre más de tres personas. Franklin apenas fue mencionada en los discursos de aceptación.
Sin embargo, la información de su trabajo perduró. Como si aquella estructura helicoidal que había puesto al descubierto le brindara una estrategia efectiva para transmitir antes de desaparecer los secretos del universo entre los que se hallaba su papel imprescindible. Décadas después, la comunidad científica reconoció ampliamente que la precisión experimental de Franklin fue decisiva para comprender la estructura del ADN, ubicándola como una figura central en la historia de la biología molecular. Y en particular en la de las mujeres olvidadas por la historia.
Gracias por leerme.
A la imbatible “inmortalidad” de las medusas Turritopsis dohrnii que son capaces de revertir su ciclo vital y volver del estado adulto al de pólipo, se suma la de los álamos clonales como el Pando cuya red genética podría tener más de 80.000 años. Entre los vertebrados, destacan las longevidades de los tiburones de Groenlandia (Somniosus microcephalus), algunos de los cuales pueden superar los 500 años de edad (eso sí, llevando una slow life con un desplazamiento muy lento y manteniéndose prácticamente ciegos al mundo).
Por ejemplo, Makarevitch, I. et al. “Transposable elements contribute to activation of maize genes in response to abiotic stress.” Proceedings of the National Academy of Sciences 112, no. 38 (2015): 11625–11630; o Casacuberta, E. & González, J. “The impact of transposable elements in environmental adaptation.” Trends in Plant Science 18, no. 8 (2013): 443–450.



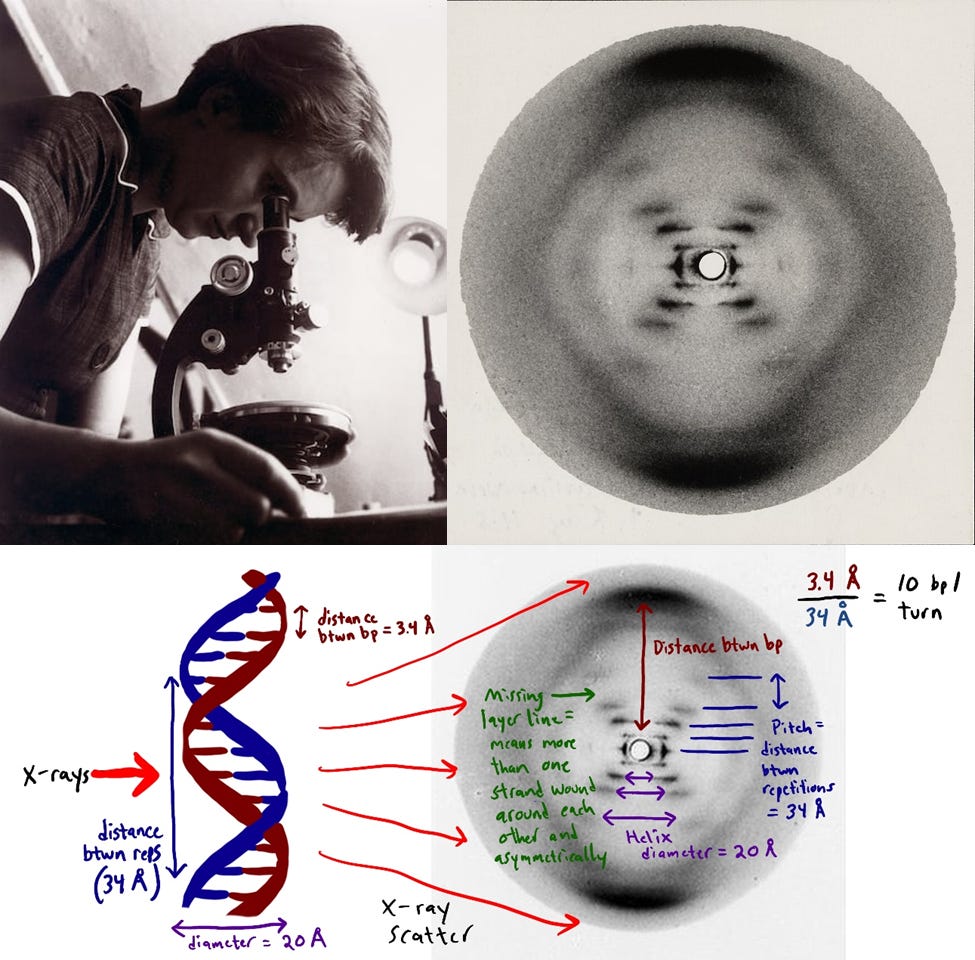
Otra científica a la que no se le reconoce su descubrimiento
Buenísimo. Gracias por seguir escribiendo!